Aktuell
Von Anfang 2017 bis September 2022 arbeitete ich bei einem großen Dienstleister in der Finanzwelt (rot, nicht blau)
als Softwareentwickler. Hier entwickelte ich Frontend- und Backendanwendungen mit JavaScript, Rest, SOAP, Java und SQL
für Oracle und DB2. Darüber hinaus konnte ich Erfahrungen mit Anwendungen auf einem Mainframe sammeln.
PA-Konzepte
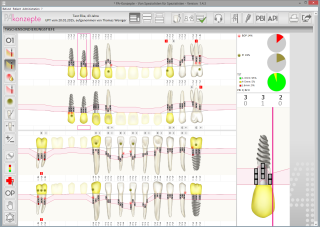
Von Anfang 2015 bis Anfang 2017 unterstützte ich das Team des Münsteraner Startups PA-Konzepte bei der Entwicklung einer parodontalen Befundsoftware.
Die Software ermöglicht Zahnarztpraxen die Aufnahme des Parodontalstatus per Sprachsteuerung (beispielsweise Taschentiefen und Informationen zu Zahnfleischblutung oder Plaque). Dadurch kann die Befundaufnahme erheblich schneller und hygienischer erfolgen als bei einem ständigen Wechsel zwischen Eingabe an der Computertastatur und Messung am Patienten.
Die Software ermöglicht Zahnarztpraxen die Aufnahme des Parodontalstatus per Sprachsteuerung (beispielsweise Taschentiefen und Informationen zu Zahnfleischblutung oder Plaque). Dadurch kann die Befundaufnahme erheblich schneller und hygienischer erfolgen als bei einem ständigen Wechsel zwischen Eingabe an der Computertastatur und Messung am Patienten.
Meine Aufgabe war die selbständige Entwicklung der Software, die zu Beginn meiner Tätigkeit nur als Prototyp existierte.
Die Entwicklung beinhaltete die Analyse von Anforderungen, der Softwareentwurf und das Implementieren neuer Funktionen.
Im Kontakt mit den Anwendern erweiterte ich den Einsatzbereich der Sprachsteuerung und verbessere vorhandene Funktionen.
Darüber hinaus war die Auswahl und Evaluation verschiedener Headset-Modelle und der Kundensupport bei technischen Problemen teil meiner Aufgaben.
Die Software ist eine Client-/Serverlösung mit Java und Hibernate.
Die Software ist eine Client-/Serverlösung mit Java und Hibernate.
Map African TB
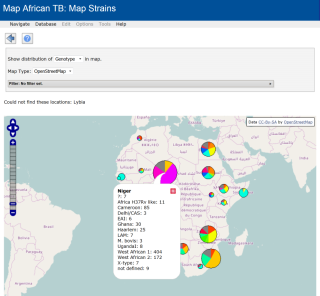
Die mittlerweile inaktive Webanwendung MLVAplus.net wurde für das Projekt Map African TB reaktiviert und wird als Datenbank
zum Zusammenführen von Isolaten verschiedener Labors verwendet.
Um mit einer größeren Datenmenge zurecht zu kommen entwickelte ich die MLVAplus.net-Anwendung weiter. Funktionen mit großem Bedarf an Rechenzeit wurden ermittelt und auf Hintergrundberechnung umgestellt wo dies notwendig war.
Weiterhin übernahm ich die Installation der Anwendung und die Wartung des Servers.
Wie bei MLVAplus.net erfolgte die Umsetzung mit Java, Servlets, JSP, JSF, AJAX, JavaScript, Hibernate und MySQL.
Um mit einer größeren Datenmenge zurecht zu kommen entwickelte ich die MLVAplus.net-Anwendung weiter. Funktionen mit großem Bedarf an Rechenzeit wurden ermittelt und auf Hintergrundberechnung umgestellt wo dies notwendig war.
Weiterhin übernahm ich die Installation der Anwendung und die Wartung des Servers.
Wie bei MLVAplus.net erfolgte die Umsetzung mit Java, Servlets, JSP, JSF, AJAX, JavaScript, Hibernate und MySQL.
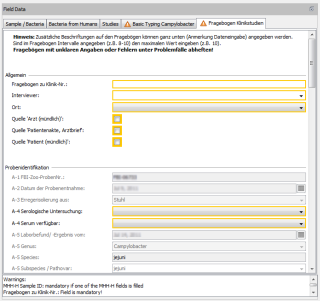
Ridom SeqSphere (Next-Generation Sequencing)
Die Software Ridom SeqSphere wurde unter meiner Mitarbeit seit 2011 zur Analyse von Next-Generation
Sequencing Daten (NGS) erweitert.
Zu meinen Aufgaben gehörte die selbständige Entwicklung von Komponenten und neuen Funktionen sowie Optimierungen in der Datenbankstruktur. Neben der Unterstützung für verschiedene Assembly-Dateiformate wurden von mir externe Assembler (Velvet, BWA) eingebunden und ein Geoinformationssystem (GIS) umgesetzt. Weiterhin gehörte die komfortable Anbindung von Webservices an die Software zu meinem Aufgabenbereich.
Die Software ist als Client-/Server-Anwendung mit Java, Swing und Hibernate realisiert.
 Weitere Informationen
Weitere Informationen
Zu meinen Aufgaben gehörte die selbständige Entwicklung von Komponenten und neuen Funktionen sowie Optimierungen in der Datenbankstruktur. Neben der Unterstützung für verschiedene Assembly-Dateiformate wurden von mir externe Assembler (Velvet, BWA) eingebunden und ein Geoinformationssystem (GIS) umgesetzt. Weiterhin gehörte die komfortable Anbindung von Webservices an die Software zu meinem Aufgabenbereich.
Die Software ist als Client-/Server-Anwendung mit Java, Swing und Hibernate realisiert.
 Weitere Informationen
Weitere Informationen
Ridom SeqSphere (FBI-Zoo)
Für den deutschlandweiten Forschungsverbund FBI-Zoo wurde von der Firma Ridom (Münster)
zusammen mit dem Universitätsklinikum Münster die Software SeqSphere zur Speicherung von
epidemiologischen Daten und DNA-Sequenzdaten entwickelt.
Meine Aufgabe am Universitätsklinikum Münster war von 2008-2011 der Entwurf und die Entwicklung neuer Komponenten, die speziell für das Verbundprojekt benötigt wurden. Darüber hinaus war auch die Administration des Servers und die Schulung der Mitarbeiter der Projektpartner meine Aufgabe.
Die Software ist als Client-/Server-Anwendung mit Java, Swing und Hibernate realisiert.
 Weitere Informationen
Weitere Informationen
Meine Aufgabe am Universitätsklinikum Münster war von 2008-2011 der Entwurf und die Entwicklung neuer Komponenten, die speziell für das Verbundprojekt benötigt wurden. Darüber hinaus war auch die Administration des Servers und die Schulung der Mitarbeiter der Projektpartner meine Aufgabe.
Die Software ist als Client-/Server-Anwendung mit Java, Swing und Hibernate realisiert.
 Weitere Informationen
Weitere Informationen
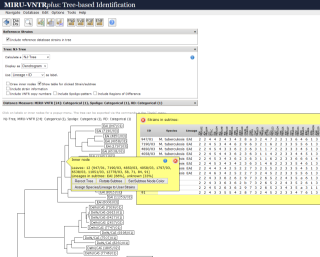
MLVAplus.net
Der große Erfolg der MIRU-VNTRplus Anwendung machte eine Verallgemeinerung der
Anwendung für weitere Erreger und Typisierungsarten wünschenswert. Diesen Wunsch habe ich in der
MLVAplus.net Anwendung umgesetzt, die ich in den Jahren 2008-2011 während meiner Zeit als
PostDoc am Universitätsklinikum Münster selbständig entwickelt habe.
MLVAplus.net ist eine Erweiterung von MIRU-VNTRplus für beliebige Spezies und Typisierungsdaten.
Die Realisierung erfolgte mit Java, Servlets, JSP, JSF, AJAX, JavaScript, Hibernate, JAXB und MySQL.
 Weitere Informationen
Weitere Informationen
MLVAplus.net ist eine Erweiterung von MIRU-VNTRplus für beliebige Spezies und Typisierungsdaten.
Die Realisierung erfolgte mit Java, Servlets, JSP, JSF, AJAX, JavaScript, Hibernate, JAXB und MySQL.
 Weitere Informationen
Weitere Informationen
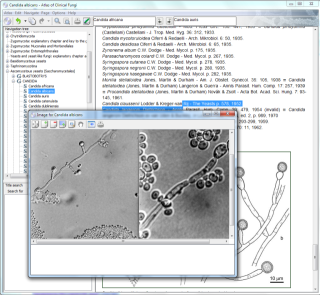
Atlas of Clinical Fungi (online & CD version)
Das Buch Atlas of Clinical Fungi (G. S. de Hoog, Gene J. Cuarro, M. J. Figueras) wurde basierend
auf den WordPerfect-Quellen durch mich im Jahre 2004 in XML-Seiten konvertiert.
Einen existierender XML-Editor (XMLmind XML Editor) habe ich in den folgenden Jahren mit Funktionen zum Bearbeiten dieser speziellen XML-Seiten erweitert.
Die XML-Seiten wurden in HTML-Seiten konvertiert und können in einer von mir entwickelten Windows Anwendung oder seit 2013 über eine Webanwendung auch online im Webbrowser angezeigt werden.
Die Umsetzung erfolgte mit Java und Swing, bzw. durch eine JavaServer Faces (JSF) Webanwendung unter Verwendung einer MySQL-Datenbank und Hibernate.
 Weitere Informationen
Weitere Informationen
Einen existierender XML-Editor (XMLmind XML Editor) habe ich in den folgenden Jahren mit Funktionen zum Bearbeiten dieser speziellen XML-Seiten erweitert.
Die XML-Seiten wurden in HTML-Seiten konvertiert und können in einer von mir entwickelten Windows Anwendung oder seit 2013 über eine Webanwendung auch online im Webbrowser angezeigt werden.
Die Umsetzung erfolgte mit Java und Swing, bzw. durch eine JavaServer Faces (JSF) Webanwendung unter Verwendung einer MySQL-Datenbank und Hibernate.
 Weitere Informationen
Weitere Informationen
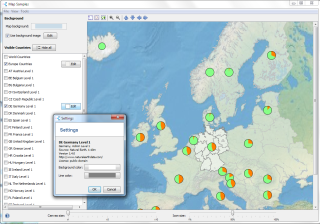
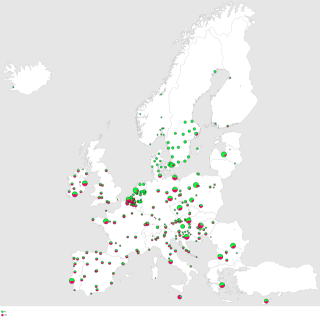
MapWeb
Für verschiedene Projekte benötigte ich eine Komponente zur Anzeige von Karten,
sowohl für Java-Programme als auch für Webanwendungen. MapWeb ist eine Sammlung von Komponenten
zur Anzeige von Kartendaten mit Java.
 Weitere Informationen
Weitere Informationen
 Weitere Informationen
Weitere Informationen
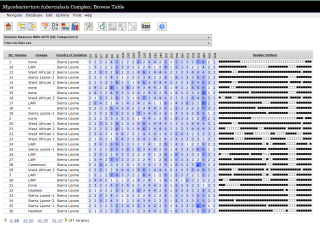
MIRU-VNTRplus
Die Typisierung von Bakterien zur Identifizierung von verbreiteten Isolaten mit gleichem genetischem
Fingerabdruck ist für die epidemiologische Überwachung von großer Bedeutung. Für Mycobacterium
tuberculosis (dem Erreger der Tuberkulose, TB) und ähnlichen Erregern ist die MIRU-VNTR Typisierung
weit verbreitet. Die Methode erlaubt auch die Zuordnung der Erreger in Untergruppen (Lineages).
Zusammen mit führenden Wissenschaftlern im Bereich der MIRU-VNTR-Typisierung habe ich am Universitätsklinikum Münster in den Jahren 2006-2008 eine Webanwendung entwickelt, welche die Analyse von MIRU-VNTR Daten und die Zuordnung von Isolaten zu Lineages ermöglicht. Die Planung und Umsetzung der Webanwendung wurde von mir im Rahmen meiner Dissertation selbständig durchgeführt.
Die Umsetzung erfolgte mit mit Java, Servlets, JSP, JSF, AJAX und JavaScript.
 Weitere Informationen
Weitere Informationen
Zusammen mit führenden Wissenschaftlern im Bereich der MIRU-VNTR-Typisierung habe ich am Universitätsklinikum Münster in den Jahren 2006-2008 eine Webanwendung entwickelt, welche die Analyse von MIRU-VNTR Daten und die Zuordnung von Isolaten zu Lineages ermöglicht. Die Planung und Umsetzung der Webanwendung wurde von mir im Rahmen meiner Dissertation selbständig durchgeführt.
Die Umsetzung erfolgte mit mit Java, Servlets, JSP, JSF, AJAX und JavaScript.
 Weitere Informationen
Weitere Informationen